M1 MABS BBS Math TD Proba
From silico.biotoul.fr
(Difference between revisions)
m (→Vraissemblance) |
m (→Vraissemblance) |
||
| Line 28: | Line 28: | ||
[[Media:Bsubtilis_RBS.fasta|Séquences]] upstream du codon start chez ''B. subtilis''. | [[Media:Bsubtilis_RBS.fasta|Séquences]] upstream du codon start chez ''B. subtilis''. | ||
| + | |||
| + | Conservation du motif RBS. Pour s'en convaincre, on peut utiliser [http://weblogo.threeplusone.com/ WebLogo]. | ||
[[Media:Maths Proba Alignement RBS.txt|Alignement]] de séquences RBS de ''B. subtilis''. | [[Media:Maths Proba Alignement RBS.txt|Alignement]] de séquences RBS de ''B. subtilis''. | ||
[[Media:Maths Proba Sequence test.txt|Séquence]] test | [[Media:Maths Proba Sequence test.txt|Séquence]] test | ||
Revision as of 07:38, 28 October 2011
Loi hypergéométrique
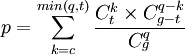
appliquée à la sur-représentation d'une annotation dans un ensemble de gènes, c'est-à-dire à la comparaison de 2 ensembles :
- c: nombre de gènes communs
- q: nombre de gènes du premier ensemble (query par exemple gènes différentiellement exprimés ou co-exprimés)
- t: nombre de gènes du deuxième ensemble (target par exemple gènes annotatés 'biosynthèse des acides aminés')
- g: nombre de gènes dans le génome
A quoi correspondent 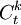 ?
? 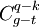 et
et 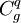 ?
?
Rappel : Combinaisons:
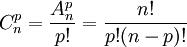
- Calculer la p-valeur pour c=30, q=100, t=300 et g=20000
- Quelle est le plus grand nombre x pour lequel vous pouvez calculer x! ?
Vraissemblance
Rappel :
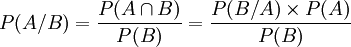
Séquences upstream du codon start chez B. subtilis.
Conservation du motif RBS. Pour s'en convaincre, on peut utiliser WebLogo.
Alignement de séquences RBS de B. subtilis.
Séquence test



